RU2386698C1 - Method of identifying transgenic dna sequences in plant material and products based on plant material - Google Patents
Method of identifying transgenic dna sequences in plant material and products based on plant material Download PDFInfo
- Publication number
- RU2386698C1 RU2386698C1 RU2008146091/13A RU2008146091A RU2386698C1 RU 2386698 C1 RU2386698 C1 RU 2386698C1 RU 2008146091/13 A RU2008146091/13 A RU 2008146091/13A RU 2008146091 A RU2008146091 A RU 2008146091A RU 2386698 C1 RU2386698 C1 RU 2386698C1
- Authority
- RU
- Russia
- Prior art keywords
- pcr
- amplification
- plant material
- dna sequences
- products
- Prior art date
Links
- 230000009261 transgenic effect Effects 0.000 title claims abstract description 18
- 239000000463 material Substances 0.000 title claims abstract description 15
- 108091028043 Nucleic acid sequence Proteins 0.000 title claims abstract description 12
- 238000000034 method Methods 0.000 title claims description 10
- 230000003321 amplification Effects 0.000 claims abstract description 24
- 238000003199 nucleic acid amplification method Methods 0.000 claims abstract description 24
- 239000000523 sample Substances 0.000 claims abstract description 17
- 108020004414 DNA Proteins 0.000 claims abstract description 14
- 238000004458 analytical method Methods 0.000 claims abstract description 11
- 238000003752 polymerase chain reaction Methods 0.000 claims description 26
- 238000001514 detection method Methods 0.000 claims description 8
- 108091034117 Oligonucleotide Proteins 0.000 claims description 7
- JLCPHMBAVCMARE-UHFFFAOYSA-N [3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-[[3-[[3-[[3-[[3-[[3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-[[5-(2-amino-6-oxo-1H-purin-9-yl)-3-hydroxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxyoxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(5-methyl-2,4-dioxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(6-aminopurin-9-yl)oxolan-2-yl]methoxy-hydroxyphosphoryl]oxy-5-(4-amino-2-oxopyrimidin-1-yl)oxolan-2-yl]methyl [5-(6-aminopurin-9-yl)-2-(hydroxymethyl)oxolan-3-yl] hydrogen phosphate Polymers Cc1cn(C2CC(OP(O)(=O)OCC3OC(CC3OP(O)(=O)OCC3OC(CC3O)n3cnc4c3nc(N)[nH]c4=O)n3cnc4c3nc(N)[nH]c4=O)C(COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3COP(O)(=O)OC3CC(OC3CO)n3cnc4c(N)ncnc34)n3ccc(N)nc3=O)n3cnc4c(N)ncnc34)n3ccc(N)nc3=O)n3ccc(N)nc3=O)n3ccc(N)nc3=O)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cc(C)c(=O)[nH]c3=O)n3cc(C)c(=O)[nH]c3=O)n3ccc(N)nc3=O)n3cc(C)c(=O)[nH]c3=O)n3cnc4c3nc(N)[nH]c4=O)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)n3cnc4c(N)ncnc34)O2)c(=O)[nH]c1=O JLCPHMBAVCMARE-UHFFFAOYSA-N 0.000 claims description 7
- 230000000295 complement effect Effects 0.000 claims description 5
- 238000012408 PCR amplification Methods 0.000 claims description 3
- 239000003153 chemical reaction reagent Substances 0.000 abstract description 9
- 238000000018 DNA microarray Methods 0.000 abstract description 4
- 238000011109 contamination Methods 0.000 abstract description 4
- 239000000203 mixture Substances 0.000 abstract description 4
- 108020004635 Complementary DNA Proteins 0.000 abstract 1
- 238000010804 cDNA synthesis Methods 0.000 abstract 1
- 239000002299 complementary DNA Substances 0.000 abstract 1
- 238000003745 diagnosis Methods 0.000 abstract 1
- 230000000694 effects Effects 0.000 abstract 1
- 239000012188 paraffin wax Substances 0.000 abstract 1
- 239000000126 substance Substances 0.000 abstract 1
- 241000196324 Embryophyta Species 0.000 description 10
- 244000068988 Glycine max Species 0.000 description 3
- 235000010469 Glycine max Nutrition 0.000 description 3
- 108010006785 Taq Polymerase Proteins 0.000 description 3
- 244000046052 Phaseolus vulgaris Species 0.000 description 2
- 235000010627 Phaseolus vulgaris Nutrition 0.000 description 2
- 238000000137 annealing Methods 0.000 description 2
- 238000004925 denaturation Methods 0.000 description 2
- 230000036425 denaturation Effects 0.000 description 2
- 239000013642 negative control Substances 0.000 description 2
- 239000011541 reaction mixture Substances 0.000 description 2
- 238000012360 testing method Methods 0.000 description 2
- 238000012546 transfer Methods 0.000 description 2
- QKNYBSVHEMOAJP-UHFFFAOYSA-N 2-amino-2-(hydroxymethyl)propane-1,3-diol;hydron;chloride Chemical compound Cl.OCC(N)(CO)CO QKNYBSVHEMOAJP-UHFFFAOYSA-N 0.000 description 1
- 108091093088 Amplicon Proteins 0.000 description 1
- 230000004544 DNA amplification Effects 0.000 description 1
- 238000009007 Diagnostic Kit Methods 0.000 description 1
- 101100288095 Klebsiella pneumoniae neo gene Proteins 0.000 description 1
- 108020005187 Oligonucleotide Probes Proteins 0.000 description 1
- 238000013459 approach Methods 0.000 description 1
- 238000010835 comparative analysis Methods 0.000 description 1
- 150000001875 compounds Chemical class 0.000 description 1
- 230000007613 environmental effect Effects 0.000 description 1
- 235000013305 food Nutrition 0.000 description 1
- 239000012634 fragment Substances 0.000 description 1
- 230000002068 genetic effect Effects 0.000 description 1
- 238000010353 genetic engineering Methods 0.000 description 1
- 101150054900 gus gene Proteins 0.000 description 1
- 238000010438 heat treatment Methods 0.000 description 1
- 238000003780 insertion Methods 0.000 description 1
- 230000037431 insertion Effects 0.000 description 1
- 239000002773 nucleotide Substances 0.000 description 1
- 125000003729 nucleotide group Chemical group 0.000 description 1
- 239000002751 oligonucleotide probe Substances 0.000 description 1
- 239000013641 positive control Substances 0.000 description 1
- 108090000623 proteins and genes Proteins 0.000 description 1
- 230000002285 radioactive effect Effects 0.000 description 1
- 238000010561 standard procedure Methods 0.000 description 1
- 231100000331 toxic Toxicity 0.000 description 1
- 230000002588 toxic effect Effects 0.000 description 1
- 230000009466 transformation Effects 0.000 description 1
Landscapes
- Measuring Or Testing Involving Enzymes Or Micro-Organisms (AREA)
Abstract
Description
Область примененияApplication area
Изобретение относится к области генной инженерии растений, молекулярной биологии, биобезопасности пищевых продуктов, фитобиотехнологии и защите окружающей среды. Изобретение может быть использовано для выявления и идентификации типичных инсерций ДНК, используемых при генетической трансформации растений, в генетически модифицированном растительном материале и продуктах на его основе.The invention relates to the field of plant genetic engineering, molecular biology, food biosafety, phytobiotechnology and environmental protection. The invention can be used to identify and identify typical DNA insertions used in the genetic transformation of plants in genetically modified plant material and products based on it.
Уровень техникиState of the art
Для обнаружения трансгенных компонентов растительного происхождения известен способ анализа ДНК с применением метода полимеразной цепной реакции (ПЦР) с использованием специфических праймеров, комплиментарных трансгенным последовательностям ДНК (Lipp M., Brodmann P., Pietsch K., Pauwels J., Anklam E. Journal of АОАС International, 1999, vol.82, №4, рр.923-928).To detect transgenic components of plant origin, a DNA analysis method using the polymerase chain reaction (PCR) method using specific primers complementary to transgenic DNA sequences is known (Lipp M., Brodmann P., Pietsch K., Pauwels J., Anklam E. Journal of AOAC International, 1999, vol. 82, No. 4, pp. 923-928).
Наиболее близким способом является способ идентификации трансгенных последовательностей ДНК в растительном материале и продуктах на основе такого материала, предполагающий использование биочипа для анализа результатов ПЦР. (Патент РФ 2270254, Мирзабеков А.Д., Грядунов Д.А., Михайлович В.М., Заседателев А.С., Романов Г.А., Кузнецов В.В., Цыденедамбаев В.Д., Митрохин И.А., Крылова Е.М., опубл. 20.02.2006).The closest method is a method for identifying transgenic DNA sequences in plant material and products based on such material, involving the use of a biochip to analyze PCR results. (RF patent 2270254, Mirzabekov A.D., Gryadunov D.A., Mikhailovich V.M., Zasedatelev A.S., Romanov G.A., Kuznetsov V.V., Tsydenedambaev V.D., Mitrokhin I. A., Krylova E.M., publ. 02.20.2006).
Основным недостатком этого способа является необходимость переноса амплификата после проведения ПЦР в ячейки биочипов, что создает предпосылку для загрязнения реактивов и лабораторного оборудования продуктами ПЦР и может привести к получению ложных результатов анализа.The main disadvantage of this method is the need to transfer the amplification after PCR to the biochip cells, which creates the prerequisite for contamination of reagents and laboratory equipment with PCR products and can lead to false analysis results.
Кроме того, нельзя использовать заранее приготовленные пробирки со смесью для амплификации.In addition, pre-prepared tubes with a mixture for amplification cannot be used.
ЗадачаA task
Задачей настоящего изобретения является создание нового способа идентификации трансгенных последовательностей ДНК в растительном материале и продуктах на основе этого материала для устранения вышеуказанных недостатков.The present invention is the creation of a new method for identifying transgenic DNA sequences in plant material and products based on this material to eliminate the above disadvantages.
Раскрытие изобретенияDisclosure of invention
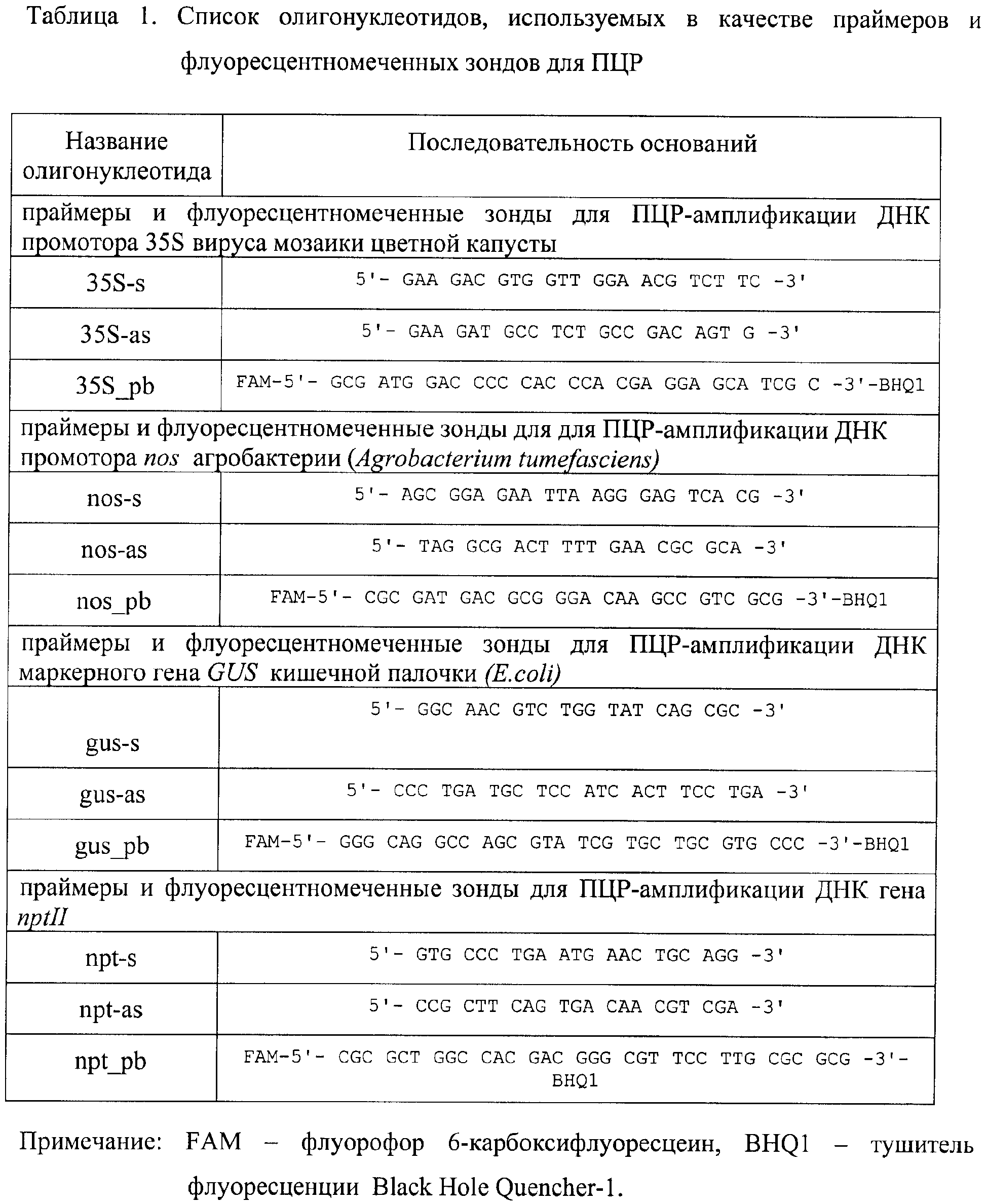
Эта задача решается новым способом идентификации трансгенных последовательностей ДНК в растительном материале и продуктах на основе этого материала, включающим анализ ДНК при помощи ПЦР с использованием набора олигонуклеотидов - специфических праймеров и флуоресцентномеченых зондов, комплиментарных этим последовательностям, и детекцию результатов ПЦР, причем ПЦР-амплификацию проводят с использованием набора олигонуклеотидов (таблица 1), с детекцией результатов амплификации в закрытых амплификационных пробирках.This problem is solved by a new method for identifying transgenic DNA sequences in plant material and products based on this material, including DNA analysis by PCR using a set of oligonucleotides - specific primers and fluorescently labeled probes complementary to these sequences, and detection of PCR results, and PCR amplification is carried out using a set of oligonucleotides (table 1), with the detection of amplification results in closed amplification tubes.
Сущность изобретенияSUMMARY OF THE INVENTION
Сущность изобретения заключается в новом подходе для обнаружения трансгенных последовательностей ДНК в растительном материале и продуктах на основе этого материала. Заявляемый способ основан на проведении ПЦР с использованием специфических праймеров и флуоресцентномеченых зондов, комплиментарных трансгенным последовательностям ДНК (таблица 1), с последующей детекцией продуктов амплификации в закрытых амплификационных пробирках с помощью флуоресцентного ПЦР-детектора. Ключевым элементом заявляемого способа является использование флуоресцентномеченых зондов, представляющих собой олигонуклеотиды, меченные молекулами флуорофора и гасителя флуоресценции. Зонды добавляют в реакционную смесь наряду с праймерами и другими компонентами реакции. В ходе ПЦР флуоресцентномеченый зонд гибридизуется на специфических ампликонах и разрушается Taq-полимеразой, в результате чего флуорофор оказывается свободным от гасителя. Таким образом, уровень флуоресценции в амплификационных пробирках возрастает пропорционально количеству образовавшихся специфических продуктов ПЦР.The essence of the invention lies in a new approach for the detection of transgenic DNA sequences in plant material and products based on this material. The inventive method is based on PCR using specific primers and fluorescently labeled probes complementary to transgenic DNA sequences (table 1), followed by detection of amplification products in closed amplification tubes using a fluorescence PCR detector. A key element of the proposed method is the use of fluorescently labeled probes, which are oligonucleotides labeled with fluorophore and fluorescence quencher molecules. Probes are added to the reaction mixture along with primers and other components of the reaction. During PCR, the fluorescently labeled probe hybridizes to specific amplicons and is destroyed by Taq polymerase, as a result of which the fluorophore is free from the quencher. Thus, the level of fluorescence in amplification tubes increases in proportion to the number of specific PCR products formed.
Сопоставительный анализ с прототипом позволяет сделать вывод, что новизна и изобретательский шаг заявляемого изобретения заключается в том, что проведение ПЦР с использованием набора олигонуклеотидов (таблица 1) и детекция результатов ПЦР в закрытых амплификационных пробирках полностью исключает загрязнение реактивов и оборудования продуктами ПЦР и предотвращает появление ложных результатов анализа.Comparative analysis with the prototype allows us to conclude that the novelty and inventive step of the claimed invention lies in the fact that PCR using a set of oligonucleotides (table 1) and detection of PCR results in closed amplification tubes completely eliminates contamination of reagents and equipment with PCR products and prevents the appearance of false analysis results.
Осуществление изобретенияThe implementation of the invention
Принципиальная схема обнаружения фрагментов трансгенной ДНКThe concept of detecting fragments of transgenic DNA
ДНК, выделенную из образца, добавляют к смеси для амплификации, содержащей праймеры и флуоресцентномеченые зонды, специфичные к трансгенным последовательностям, затем проводят амплификацию ДНК с помощью амплификатора, а детекцию результатов амплификации - в закрытых амплификационных пробирках осуществляют по завершении ПЦР с помощью флуоресцентного ПЦР-детектора.DNA extracted from the sample is added to the amplification mixture containing primers and fluorescently labeled probes specific for transgenic sequences, then the amplification of the DNA is carried out using an amplifier, and the amplification results are detected in closed amplification tubes after completion of PCR using a fluorescent PCR detector .
Пример конкретного выполненияConcrete example
Анализ присутствия чужеродных последовательностей ДНК в растительном материале (ГМ соя линии 40-3-2).Analysis of the presence of foreign DNA sequences in plant material (GM soybean line 40-3-2).
ДНК из бобов ГМ сои линии 40-3-2 выделяют стандартным методом. Равное количество ДНК (5 мкл), выделенной из каждого исследуемого образца, анализируют при помощи четырех комплектов реагентов для амплификации ДНК, отличающихся друг от друга наборами праймеров и флуоресцентномеченых зондов, специфичных по отношению к промотору 35S, промотору nos, гену gus и гену nptII, соответственно. Последовательности праймеров и олигонуклеотидных зондов приведены в таблице 1. Помимо ДНК исследуемых образцов с помощью указанных комплектов реагентов анализируют положительный и отрицательный контрольный образцы.DNA from beans of the GM soybean line 40-3-2 is isolated by the standard method. An equal amount of DNA (5 μl) isolated from each test sample was analyzed using four sets of DNA amplification reagents, differing in sets of primers and fluorescently labeled probes specific for the 35S promoter, nos promoter, gus gene, and nptII gene, respectively. The sequences of primers and oligonucleotide probes are shown in table 1. In addition to the DNA of the studied samples, the positive and negative control samples are analyzed using the indicated sets of reagents.
Указанные комплекты реагентов для амплификации ДНК помимо специфических праймеров (по 14 пМ каждого) и флуоресцентномеченых зондов (по 7 пМ) содержат следующие общие компоненты: 6 мМ каждого dNTP; 84 мМ TRIS-HCl (рН 8,6); 21 мМ (NH4)2SO4; 3,1 мМ - MgCl2 а также 5 единиц Taq-полимеразы. Общий объем реакционной смеси составляет 35 мкл. Для каждого комплекта реагентов готовят фоновые пробирки, отличающиеся отсутствием Taq-полимеразы, в которые добавляют отрицательный контрольный образец и термоциклируют совместно с остальными пробирками.These sets of reagents for amplification of DNA in addition to specific primers (14 pM each) and fluorescently labeled probes (7 pM) contain the following common components: 6 mM of each dNTP; 84 mM TRIS-HCl (pH 8.6); 21 mM (NH 4 ) 2 SO 4 ; 3.1 mmol - MgCl 2 as well as 5 units of Taq polymerase. The total volume of the reaction mixture is 35 μl. For each set of reagents, background tubes are prepared, characterized by the absence of Taq polymerase, into which a negative control sample is added and thermocycled together with the remaining tubes.
Амплификацию проводят с помощью амплификатора "Терцик" производства ЗАО "НПФ ДНК-Технология" (Москва) при следующем температурном режиме: первоначальный прогрев при 94°С в течение 1 мин 30 сек, денатурация при 94°С - 20 сек, отжиг при 64°С - 5 сек, элонгация при 67°С - 5 сек (5 циклов), затем денатурация при 94°С - 1 сек, отжиг при 64°С - 5 сек, элонгация при 67°С - 5 сек (40 циклов).Amplification is carried out using the Tercik amplifier manufactured by NPF DNA-Technology CJSC (Moscow) at the following temperature conditions: initial heating at 94 ° С for 1 min 30 sec, denaturation at 94 ° С - 20 sec, annealing at 64 ° C - 5 sec, elongation at 67 ° C - 5 sec (5 cycles), then denaturation at 94 ° C - 1 sec, annealing at 64 ° C - 5 sec, elongation at 67 ° C - 5 sec (40 cycles).
Детекцию продуктов амплификации в закрытых пробирках проводят по завершении ПЦР с помощью флуоресцентного ПЦР-детектора «Джин». Интерпретация результатов проводится автоматически, на основании сравнения уровня флуоресценции в пробирках с уровнем флуоресценции в фоновых пробирках соответствующего комплекта реагентов. Результаты анализа отображаются на экране компьютера в виде таблицы. Выявлено существенное повышение уровня флуоресценции, то есть наличие специфических продуктов ПЦР в пробирке, содержащей набор праймеров и флуоресцентномеченых зондов, комплиментарных нуклеотидной последовательности промотора 35S, и анализируемую ДНК.Detection of amplification products in closed tubes is carried out at the end of PCR using a fluorescence PCR detector "Gene". Interpretation of the results is carried out automatically, based on a comparison of the level of fluorescence in the tubes with the level of fluorescence in the background tubes of the corresponding set of reagents. The analysis results are displayed on the computer screen in the form of a table. A significant increase in the level of fluorescence was revealed, i.e., the presence of specific PCR products in a test tube containing a set of primers and fluorescently labeled probes complementary to the 35S promoter nucleotide sequence and the analyzed DNA.
Следовательно, в результате анализа бобов ГМ сои линии 40-3-2 обнаружена трансгенная ДНК.Therefore, as a result of the analysis of beans of GM soybean line 40-3-2 detected transgenic DNA.
Результаты изобретенияThe results of the invention
Основным преимуществом предлагаемого изобретения является отсутствие необходимости переноса амплификата после проведения ПЦР в ячейки биочипов. В предлагаемом изобретении ПЦР-амплификацию проводят с использованием нового набора олигонуклеотидов (таблица 1), включающего специфические праймеры и флуоресцентномеченые зонды, а детекция результатов ПЦР проводится в закрытых амплификационных пробирках с помощью флуоресцентного ПЦР-детектора, что полностью исключает возможность загрязнения реактивов и оборудования продуктами ПЦР и предотвращает получение ложных результатов анализа.The main advantage of the invention is the absence of the need to transfer the amplification after PCR to the cells of biochips. In the present invention, PCR amplification is carried out using a new set of oligonucleotides (table 1), including specific primers and fluorescently labeled probes, and PCR results are detected in closed amplification tubes using a fluorescent PCR detector, which completely eliminates the possibility of contamination of reagents and equipment with PCR products and prevents the receipt of false analysis results.
Кроме того, предлагаемые изобретения высокотехнологичны, не требуют значительных трудовых затрат. Заранее подготовленные пробирки с запечатанной парафином смесью для амплификации хранятся длительное время (более полугода) при комнатной температуре, что позволяет использовать их в составе готовых диагностических наборов. При необходимости возможно использование дополнительных наборов праймеров и флуоресцентномеченых зондов для исследования более широкого спектра трансгенных последовательностей ДНК, применяемых при создании трансгенных растений.In addition, the proposed invention is high-tech, does not require significant labor costs. Pre-prepared tubes with a paraffin-sealed mixture for amplification are stored for a long time (more than six months) at room temperature, which allows them to be used as part of ready-made diagnostic kits. If necessary, it is possible to use additional sets of primers and fluorescently labeled probes to study a wider range of transgenic DNA sequences used to create transgenic plants.
Предлагаемые изобретения не представляют опасности для здоровья персонала и для окружающей среды, так как не связаны с применением токсичных или радиоактивных соединений.The proposed invention does not pose a risk to the health of personnel and the environment, as it is not associated with the use of toxic or radioactive compounds.
Claims (1)
Priority Applications (1)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| RU2008146091/13A RU2386698C1 (en) | 2008-11-24 | 2008-11-24 | Method of identifying transgenic dna sequences in plant material and products based on plant material |
Applications Claiming Priority (1)
| Application Number | Priority Date | Filing Date | Title |
|---|---|---|---|
| RU2008146091/13A RU2386698C1 (en) | 2008-11-24 | 2008-11-24 | Method of identifying transgenic dna sequences in plant material and products based on plant material |
Publications (1)
| Publication Number | Publication Date |
|---|---|
| RU2386698C1 true RU2386698C1 (en) | 2010-04-20 |
Family
ID=46275179
Family Applications (1)
| Application Number | Title | Priority Date | Filing Date |
|---|---|---|---|
| RU2008146091/13A RU2386698C1 (en) | 2008-11-24 | 2008-11-24 | Method of identifying transgenic dna sequences in plant material and products based on plant material |
Country Status (1)
| Country | Link |
|---|---|
| RU (1) | RU2386698C1 (en) |
Cited By (1)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| RU2607372C1 (en) * | 2015-12-15 | 2017-01-10 | Федеральное государственное бюджетное образовательное учреждение высшего образования "Санкт-Петербургский государственный университет" (СПбГУ) | Diagnostic technique for plant material for transgenicity |
Citations (7)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| RU2093582C1 (en) * | 1993-07-21 | 1997-10-20 | Институт молекулярной генетики РАН | Method of genome dactyloscopy |
| RU2182176C2 (en) * | 1991-09-24 | 2002-05-10 | Кейгене Н.В. | Method of selective amplification, oligonucleotide and set for selective amplification |
| CN1385541A (en) * | 2002-05-17 | 2002-12-18 | 中山大学 | Method for detecting transgenic plant and products thereof |
| CN1428438A (en) * | 2001-12-28 | 2003-07-09 | 中国科学院上海生物工程研究中心 | Transgenic agricultural product detection kit |
| RU2265668C1 (en) * | 2004-09-15 | 2005-12-10 | Общество с ограниченной ответственностью Инновационная Корпорация "БИОЗАЩИТА" | Set of primers for detection and/or identification of transgene dna sequences in vegetable material and product comprising thereof (variants), primer (variants), pair of primers (variants), method for detection and/or identification with their using (variants) and device for realization of method |
| RU2270254C2 (en) * | 2004-04-30 | 2006-02-20 | Институт Молекулярной Биологии Им. В.А. Энгельгардта Российской Академии Наук | Identification of transgenic dna sequences in plant material and products made of the same, oligonucleotide kit and bioarray therefor |
| RU2279482C2 (en) * | 1999-04-01 | 2006-07-10 | МакДЖИЛЛ ЮНИВЕРСИТИ | Transposone-based new kind of genetic marker |
-
2008
- 2008-11-24 RU RU2008146091/13A patent/RU2386698C1/en not_active IP Right Cessation
Patent Citations (7)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| RU2182176C2 (en) * | 1991-09-24 | 2002-05-10 | Кейгене Н.В. | Method of selective amplification, oligonucleotide and set for selective amplification |
| RU2093582C1 (en) * | 1993-07-21 | 1997-10-20 | Институт молекулярной генетики РАН | Method of genome dactyloscopy |
| RU2279482C2 (en) * | 1999-04-01 | 2006-07-10 | МакДЖИЛЛ ЮНИВЕРСИТИ | Transposone-based new kind of genetic marker |
| CN1428438A (en) * | 2001-12-28 | 2003-07-09 | 中国科学院上海生物工程研究中心 | Transgenic agricultural product detection kit |
| CN1385541A (en) * | 2002-05-17 | 2002-12-18 | 中山大学 | Method for detecting transgenic plant and products thereof |
| RU2270254C2 (en) * | 2004-04-30 | 2006-02-20 | Институт Молекулярной Биологии Им. В.А. Энгельгардта Российской Академии Наук | Identification of transgenic dna sequences in plant material and products made of the same, oligonucleotide kit and bioarray therefor |
| RU2265668C1 (en) * | 2004-09-15 | 2005-12-10 | Общество с ограниченной ответственностью Инновационная Корпорация "БИОЗАЩИТА" | Set of primers for detection and/or identification of transgene dna sequences in vegetable material and product comprising thereof (variants), primer (variants), pair of primers (variants), method for detection and/or identification with their using (variants) and device for realization of method |
Non-Patent Citations (1)
| Title |
|---|
| ГОСТ Р 52174-03. Метод идентификации генетически модифицированных растений и продуктов на их основе. * |
Cited By (1)
| Publication number | Priority date | Publication date | Assignee | Title |
|---|---|---|---|---|
| RU2607372C1 (en) * | 2015-12-15 | 2017-01-10 | Федеральное государственное бюджетное образовательное учреждение высшего образования "Санкт-Петербургский государственный университет" (СПбГУ) | Diagnostic technique for plant material for transgenicity |
Similar Documents
| Publication | Publication Date | Title |
|---|---|---|
| JP2019201658A (en) | Multiplex pyrosequencing using non-interfering noise canceling polynucleotide identification tags | |
| CA2895945C (en) | Target capture system | |
| RU2270254C2 (en) | Identification of transgenic dna sequences in plant material and products made of the same, oligonucleotide kit and bioarray therefor | |
| JP2011062119A (en) | Chip for quantitatively determining biological sample | |
| US20210246499A1 (en) | Detection of short homopolymeric repeats | |
| Zhang et al. | PCR multiplexing based on a single fluorescent channel using dynamic melting curve analysis | |
| AU2015213570B2 (en) | NGS systems control and methods involving the same | |
| HK1222881A1 (en) | Improved ngs workflow | |
| US20160138099A1 (en) | Quantitative multiplexed identification of nucleic acid targets | |
| RU2386698C1 (en) | Method of identifying transgenic dna sequences in plant material and products based on plant material | |
| KR101080087B1 (en) | Chip for cell amplification reaction and isothermal amplification device using the same | |
| CN102899402B (en) | Vibrio shilonii multiple virulence factor GeXP rapid detection kit and detection method thereof | |
| KR101288419B1 (en) | Primer composition and kit for isothermal amplification reaction for detecting Pectobacterium carotovorum subsp. comprising specific primer set, and method for detecting Pectobacterium carotovorum subsp. using the primer set | |
| JP2011062197A (en) | Quantitative method for biological sample | |
| CN102171369A (en) | Method for measuring survivin mRNA | |
| Zakeri et al. | Use of padlock probes and rolling circle amplification (RCA) for rapid identification of Trichophyton species, related to human and animal disorder | |
| CN112877460A (en) | Transgenic component high-throughput screening method, detection kit and application thereof | |
| CN104830857A (en) | Primer, probe and method for specific quantitative PCR accurate detection of genetically modified corn MON88017 strain | |
| CN102899412A (en) | Rapid detection kit and detection method for multiple virulence factor GeXP of vibrio coralliilyticus | |
| RU2607372C1 (en) | Diagnostic technique for plant material for transgenicity | |
| RU2670207C1 (en) | Set of synthetic oligonucleotides for identification of gardnerella vaginalis dna in vaginal mucosa | |
| KR20260003548A (en) | Primer set for detecting pathogens causing Dysentery in pigs and Method for detecting pathogens using the same | |
| CN115058493A (en) | DNA probe for multiple nucleic acid detection, CRISPR-reverse dot hybrid nucleic acid detection system and application | |
| CN116445596A (en) | Product and method for human genotyping and application thereof | |
| CN101812531A (en) | Escherichia coli detection kit |
Legal Events
| Date | Code | Title | Description |
|---|---|---|---|
| MM4A | The patent is invalid due to non-payment of fees |
Effective date: 20111125 |